Attività di ricerca
Le attività principali del Laboratorio sono:
- caratterizzare i profili (fenotipi) metabolici di organismi viventi vegetali ed animali
- caratterizzare i profili metabolici di cellule microbiche, vegetali, animali ed umane in relazione a mutazioni genetiche o perturbazioni biotiche o abiotiche;
- identificare nuovi biomarcatori che consentano di migliorare la diagnosi e la prognosi clinica;
- identificare nuovi bersagli metabolici nelle diverse patologie umane;
- valutare l’effetto di interventi farmacologici, dietetici o comportamentali sullo stato di salute umano ed animale;
- valutare possibili effetti collaterali di trattamenti farmacologici;
- valutare le interazioni tra dieta, microbiota intestinale e metabolismo umano ed animale in stati fisiologici e patologici;
- personalizzare gli interventi farmacologici e/o nutrizionali basati sul fenotipo metabolico dell’individuo (Medicina e Nutrizione di Precisione);
- effettuare la caratterizzazione integrata degli alimenti vegetali in relazione a origine, condizioni pedo-climatiche e agronomiche;
- identificare composti bioattivi negli alimenti;
- progettare alimenti funzionali e di valutare il loro impatto sulla salute.
- valutare le fasi di trasformazione di prodotti alimentari per l’ottimizzazione dei processi
- valutare le fasi di processi coinvolti nella economia circolare agricola.
Il team che gestisce NMLab è a disposizione per discutere potenziali esperimenti, nonchè per accordarsi su collaborazioni che includono una più avanzata analisi ed intrepretazione dei dati.
Metabolomica
La metabolomica è la caratterizzazione dell'insieme completo di metaboliti in una matrice di origine animale o vegetale, evidenziando la sua variazione in base allo stato fisiologico, evolutivo o patologico della cellula, tessuto, organo o organismo. Questa caratterizzazione permette di ricostruire la rete dei processi metabolici del sistema in studio. Le metabolomica ha applicazioni in molte aree, inclusa la salute umana e animale, la scoperta di biomarcatori, la scoperta e lo sviluppo di farmaci, la biologia vegetale, la microbiologia, la chimica degli alimenti ed il monitoraggio ambientale. La metabolomica permette di analizzare più a fondo un sistema biologico per ottenere una descrizione più dettagliata dei processi biochimici e delle loro interconnessioni.
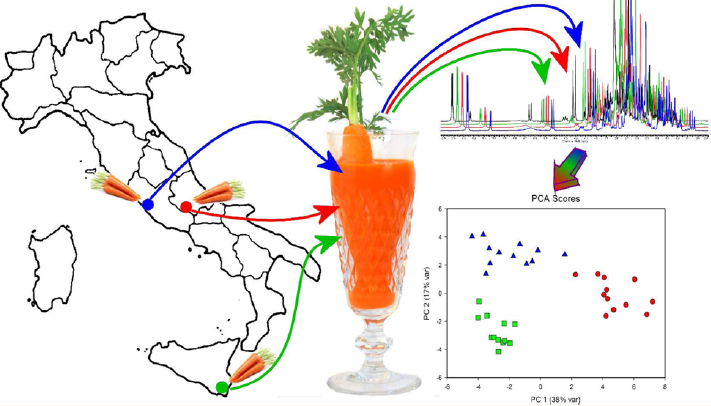
Va sottolineato che, allo stato attuale, la metabolomica basata sulla spettroscopia di Risonanza Magnetica Nucleare (RMN) effettuata dall'NMLab non può essere intesa come un strumento diagnostico o un esame clinico bensì un'indagine scientifica su popolazioni di soggetti per individuare eventuali tratti caratteristici del metabolismo che possano distinguere gruppi diversi in funzione di deteminate variazioni: non è quindi un esame diagnostico e non è applicabile a casi singoli.
La spettroscopia RMN è la tecnica preferenziale per la caratterizzazione degli aspetti strutturali e per la quantificazione di molecole in miscele complesse, che possono essere effettuate in un unico spettro senza pre-trattamento. Essa offre importanti vantaggi rispetto alle altre tecniche analitiche, che possono essere riassunti in termini di facilità di quantificazione, identificazione diretta dei metaboliti e capacità di determinare metaboliti inattesi. Infatti, l'analisi RMN di un campione consente il rilevamento simultaneo di metaboliti a basso peso molecolare presenti in una soluzione a una concentrazione superiore a 10-6 M.
L'analisi metabolomica basata sulla spettroscopia RMN è effettuata principalmente applicando metodi di analisi statistica multivariata ad un insieme di dati risultanti da spettri RMN.
Esperimenti RMN
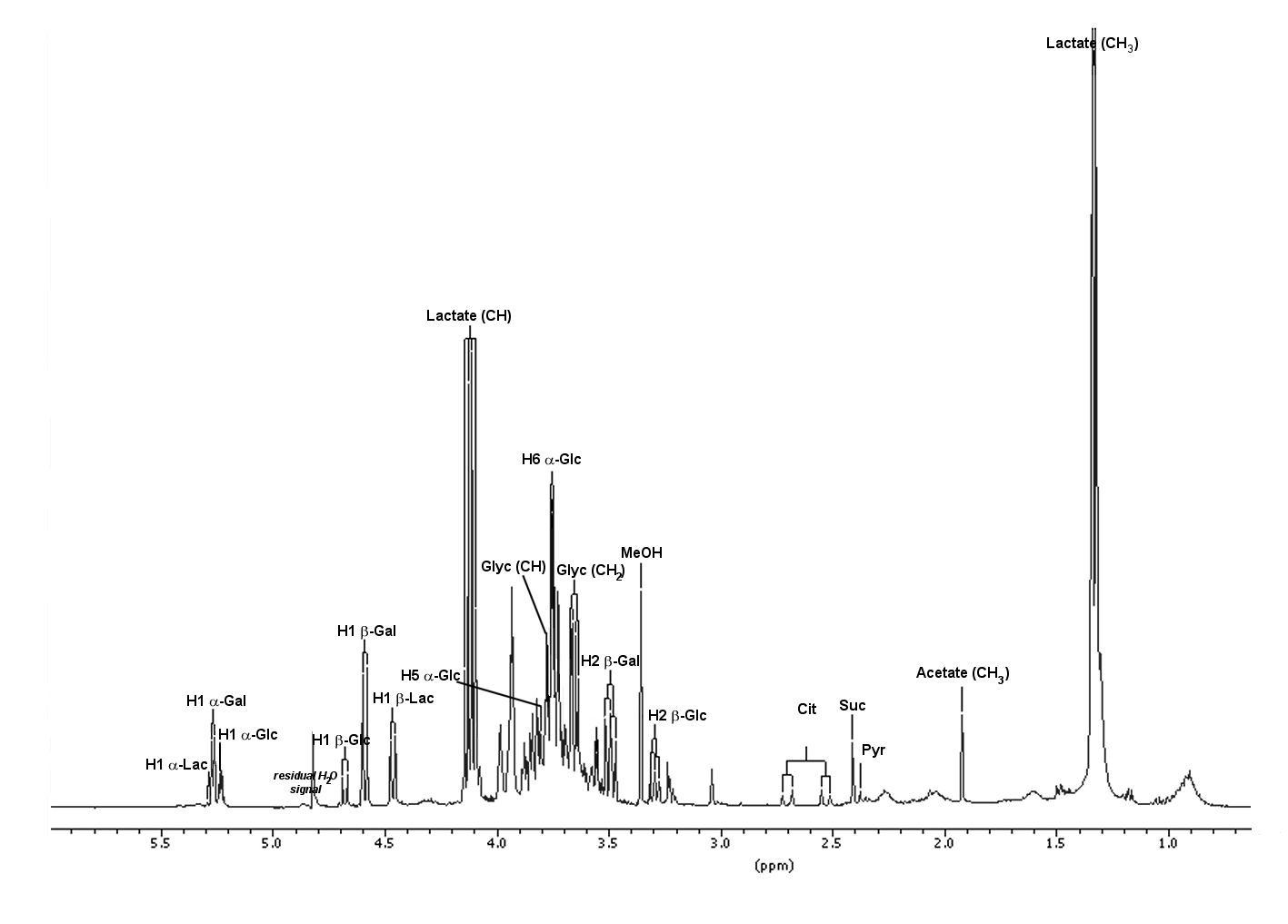
Gli spettri RMN sono costituiti da una serie di segnali di risonanza, ciascuno originato dai nuclei magneticamente equivalenti (nuclei di idrogeno per la spettroscopia 1H RMN). La loro posizione nello spettro (chemical shift) è caratteristica del gruppo chimico a cui è legato il nucleo e del suo intoro chimico, mentre le loro intensità (aree) sono proporzionali alla concentrazione del gruppo chimico e quindi della molecola. Poiché qualsiasi metabolita è composto da più di un gruppo chimico con atomi di idrogeno, ne deriva che ogni metabolita è rappresentato da più di un segnale RMN. Lo spettro 1H monodimensionale (1D) di una miscela produce quindi un insieme sovraffollato di segnali di risonanza, ovvero un'istantanea di tutti i metaboliti in esso contenuti: è spesso descritta come la sua impronta digitale, o impronta metabolica. L'assegnazione dei segnali sovrapposti può essere resa molto più semplice eseguendo esperimenti RMN bidimensionali (2D), che sviluppano la complessità dello spettro 1D in una seconda dimensione.
Analisi dei dati
La quantificazione è il passaggio che trasforma un insieme di spettri RMN in una matrice di dati. Questo obiettivo può essere raggiunto seguendo due percorsi complementari: risolvendo l’insieme dei segnali assegnando ciascuno (o la maggior parte) al corretto metabolita e misurando le intensità degli specifici picchi di interesse (targeted analysis), oppure elaborando gli spettri "tal quali" indipendentemente da qualsiasi considerazione e basandosi sulle strutture di correlazione incorporate nello spettro 1H 1D grazie alla sua ridondanza intrinseca (pattern recognition) .
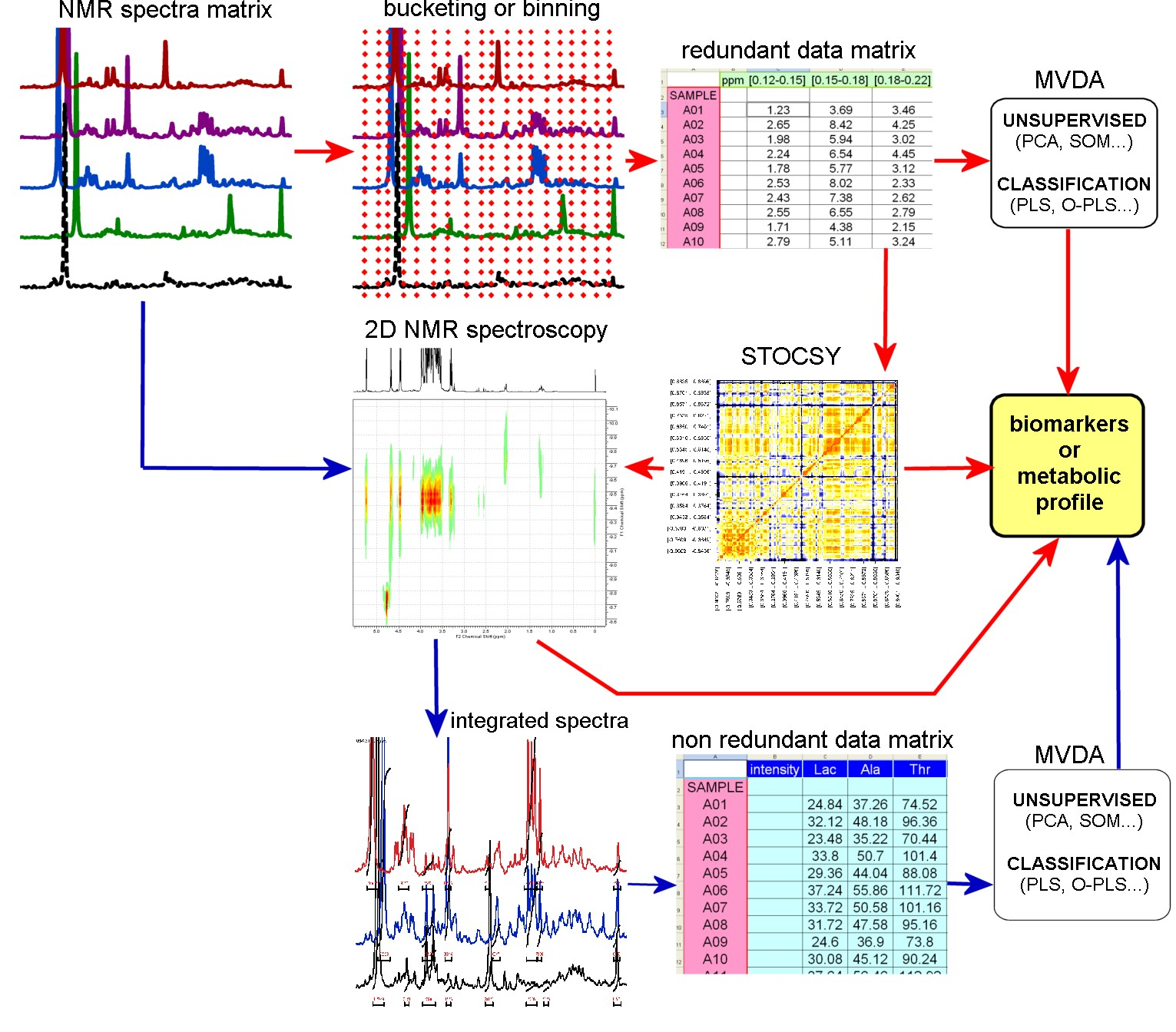
Sia la targeted analysis che la pattern recognition richiedono l'assegnazione dei segnali di risonanza ai loro metaboliti di origine. Questa procedura richiede l'abilità dell'operatore, che si può basare su una vasta gamma di tecniche 2D NMR, su spettri di riferimento, su dati di letteratura. Entrambe contribuiscono a fornire i profili metabolici del sistema e a rilevare i biomarcatori che caratterizzano i processi biologici che si verificano in esso.
Dopo questi passaggi vengono applicate le tecniche multivariate per il rilevamento - in modo unsupervised per individuare correlazioni intrinseche nel campo dati e/o la presenza di valori anomali (comunemente mediante Analisi in Componenti Principali, PCA) o supervised utilizzando variabili esterne note (come con Partial Least Squares Analysis, PLS, Orthogonal-PLS, Multiple Correspondence Analysis, MCA) o per classificazione (PLS, SIMCA, Multiway analysis ecc.)
